
-

生物通官微
陪你抓住生命科技
跳动的脉搏
玉米叶鞘斑病病原菌Epicoccum sorghinum近乎完整基因组与侵染转录组的解析
【字体: 大 中 小 】 时间:2025年02月14日 来源:Scientific Data 5.8
编辑推荐:
本研究针对中国新发玉米叶鞘斑病病原菌Epicoccum sorghinum,通过牛津纳米孔GridION和Illumina NovaSeq 6000双平台测序,获得32.69Mb近乎完整的无间隙核基因组(含12条完整染色体)及61.24kb线粒体基因组,注释出11,779个蛋白编码基因。通过时序RNA-Seq分析揭示4,058个侵染诱导基因,鉴定出效应因子、碳水化合物活性酶(CAZymes)等潜在毒力因子,为解析该病原菌的分子致病机制提供了关键资源。
玉米作为全球第二大粮食作物,其生产正面临真菌性疾病的严峻威胁。近年来,由Epicoccum sorghinum(又称Phoma sorghina)引起的玉米叶鞘斑病在中国快速蔓延,这种病原菌不仅能通过伤口侵染玉米叶片和叶鞘,还会产生具有毒性的次生代谢产物tenuazonic acid,严重威胁粮食安全。更令人担忧的是,该病原菌具有广谱寄主适应性,已在小麦、水稻等重要作物上引发类似病害。然而,科学界对其分子致病机制的认识仍存在巨大空白。
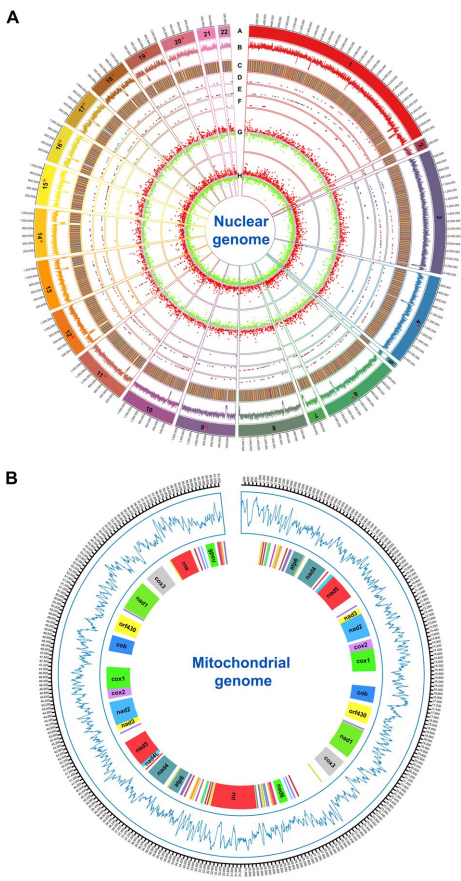
为破解这一科学难题,中国农业大学植物保护学院植物病理学系的研究团队对E. sorghinum强毒株NJC07展开了系统性研究。通过整合三代纳米孔长读长和二代Illumina短读长测序技术,研究人员成功构建了该病原菌的高质量基因组图谱――包含12条端粒到端粒完整测序的染色体,基因组大小32.69Mb,注释出11,779个蛋白编码基因。尤为重要的是,比较基因组分析发现,尽管玉米、高粱和甘蔗致病菌株间基因组相似度达91%以上,但玉米致病株NJC07特有的2,291-3,916个基因可能与其宿主适应性进化密切相关。
为揭示病原菌的侵染策略,研究团队通过时序转录组分析(48/96 hpi)鉴定出4,058个侵染诱导基因,其中CAZymes(碳水化合物活性酶)基因的差异表达模式尤为显著:纤维素酶(cellulolytic)、木质素降解酶(ligninolytic)和果胶酶(pectinolytic)等细胞壁降解酶系在侵染早期(48 hpi)即被强烈激活,而淀粉降解酶(starch-degrading)等则在后期(96 hpi)显著上调。这种时序调控模式与病原菌采用"先破壁后取食"的坏死营养型侵染策略高度吻合。
研究还发现,效应因子基因呈现两极化分布:约60%的效应因子富含半胱氨酸(>3% Cys),这类蛋白可能参与宿主免疫系统的干扰;而其余效应因子则具有典型的分泌蛋白特征(如信号肽)。通过全基因组共线性分析(图2),研究人员在NJC07特有基因组区段发现了多个次级代谢基因簇,这些基因簇可能编码宿主特异性毒素或其他致病相关化合物。
关键技术方法包括:1)采用GridION纳米孔长读长(最长157.84 kb)与NovaSeq 6000短读长(2×150 bp)双平台测序;2)运用Falcon-Canu-Pilon混合组装策略构建无间隙基因组;3)通过EVidenceModeler整合ab initio、同源预测和转录组证据进行基因注释;4)基于感染时间序列(48/96 hpi)的RNA-Seq分析差异表达基因。
主要研究结果:
基因组特征:组装获得22条核基因组contig(N50=1.66 Mb)和完整线粒体基因组(61.24 kb),BUSCO评估显示96.21%的保守真菌基因完整存在。
比较基因组学:玉米致病株NJC07与甘蔗致病株BS2-1基因组相似度达99.04%,但存在2个显著基因组重排事件。
侵染转录组:鉴定出3,357(48 hpi)和3,658(96 hpi)个上调基因,其中CAZymes和效应因子基因显著富集。
毒力因子预测:发现136个候选效应因子和428个CAZymes,包括GH(糖苷水解酶)和CE(碳水化合物酯酶)家族成员。
这项发表于《Scientific Data》的研究首次提供了E. sorghinum的高质量参考基因组,其重要意义在于:1)为理解该病原菌宿主适应性进化提供了分子基础;2)鉴定的毒力因子可作为抗病育种的潜在靶标;3)建立的侵染基因表达谱为开发新型防控策略指明了方向。随着全球气候变化背景下作物病害谱的演变,这类基础性研究将为保障粮食安全提供关键科学支撑。
 生物通微信公众号
生物通微信公众号
知名企业招聘