
-

生物通官微
陪你抓住生命科技
跳动的脉搏
生命学院李雪明课题组开发冷冻电子断层成像中基于膜展平的膜蛋白可视化和定位新方法
【字体: 大 中 小 】 时间:2025年01月14日 来源:清华园生命学院
编辑推荐:
冷冻电子断层成像(cryo-electron tomography, cryoET)技术,冷冻聚焦离子束(cryo-focused ion beam, cryoFIB)样品减薄技术,和子断层平均技术(sub-tomogram averaging, STA)的进步推动了生物大分子在细胞中的原位结构测定。这对于研究膜蛋白结构及其在细胞环境中的相互作用具有重要意义。断层扫描图像(tomogram)是三维图像,但由于低信噪比和细胞内拥挤的环境,当前的观察方法仍主要依赖查看tomogram中的二维截面。然而...
冷冻电子断层成像(cryo-electron tomography, cryoET)技术,冷冻聚焦离子束(cryo-focused ion beam, cryoFIB)样品减薄技术,和子断层平均技术(sub-tomogram averaging, STA)的进步推动了生物大分子在细胞中的原位结构测定。这对于研究膜蛋白结构及其在细胞环境中的相互作用具有重要意义。断层扫描图像(tomogram)是三维图像,但由于低信噪比和细胞内拥挤的环境,当前的观察方法仍主要依赖查看tomogram中的二维截面。然而,细胞中的膜结构通常呈弯曲形态,这使得通过二维截面难以直接观察膜表面蛋白的分布。同时,膜信号强烈的衬度也会干扰膜蛋白的识别,增加了原位观察和结构解析的难度。
2025年1月8日,清华大学生命科学学院李雪明副教授课题组在《自然通讯》(Nature Communications)杂志在线发表研究论文,题目为“MPicker:冷冻电子断层成像中膜蛋白的可视化与挑选”(MPicker: visualizing and picking membrane proteins for cryo-electron tomography)。该论文报道了一种基于“膜展平”的方法,通过在“展平tomogram”中进行操作来降低膜蛋白可视化与挑选的难度(图1)。该方法首先通过膜分割或者手动标注定位感兴趣区域(一片膜),然后在tomogram中对这片膜及其周围的区域进行变形处理,最终把这个局部区域展平为一个包含平整膜结构的新tomogram,也就是展平tomogram。在这个新生成的展平tomogram中,原本弯曲的膜会变成一个平板,膜厚度与蛋白取向局部保持不变。展平tomogram中每一层二维截面都对应一个平行于膜的等距面,使得膜表面的蛋白信号可以轻易地以二维图像的形式被展示。这起到了降维的效果,降低了膜蛋白分析的空间复杂性,改善了膜上和膜周围蛋白质的可视化效果。
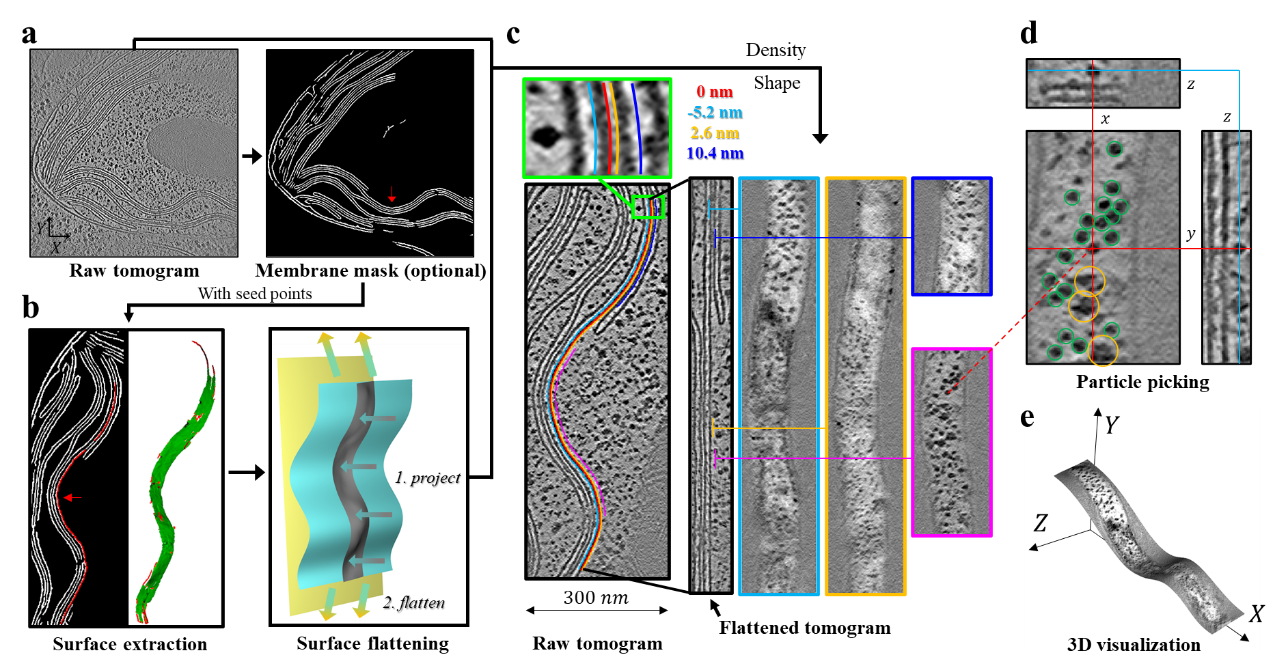
图1:MPicker软件流程图
基于膜展平方法,研究团队开发了名为MPicker的新软件,该软件能够在多种细胞切片样品的tomogram中清晰展示膜表面的蛋白分布(图2)。在展平tomogram中,用户可以更方便地识别并挑选颗粒。为了提高自动化程度,MPicker还整合了EPicker软件(一款原本用于单颗粒图像的自动颗粒挑选工具),充分利用了展平tomogram二维化的优势。除了在MPicker中进行操作,用户也可以灵活地使用其它软件在展平tomogram中进行颗粒挑选。

图2:使用MPicker对类囊体膜进行展平
MPicker还可以提供每个颗粒的初始取向用于辅助膜蛋白STA的计算。除了常规的膜法向量,用户还可以方便地通过MPicker在展平tomogram中标注蛋白在膜表面的面内取向,从而利用更强的角度约束来辅助STA的计算。为提高取向确定的自动化程度,研究团队将膜蛋白沿膜法向量投影,并进行了改造的二维分类,从而更高效地获得每个颗粒的精准取向信息。通过这一方法,团队使用4套tomogram数据成功解析了衣藻PSII-LHCII超复合物的低分辨原位结构(图3),并将结果上传至EMDB数据库(EMD-61019)。
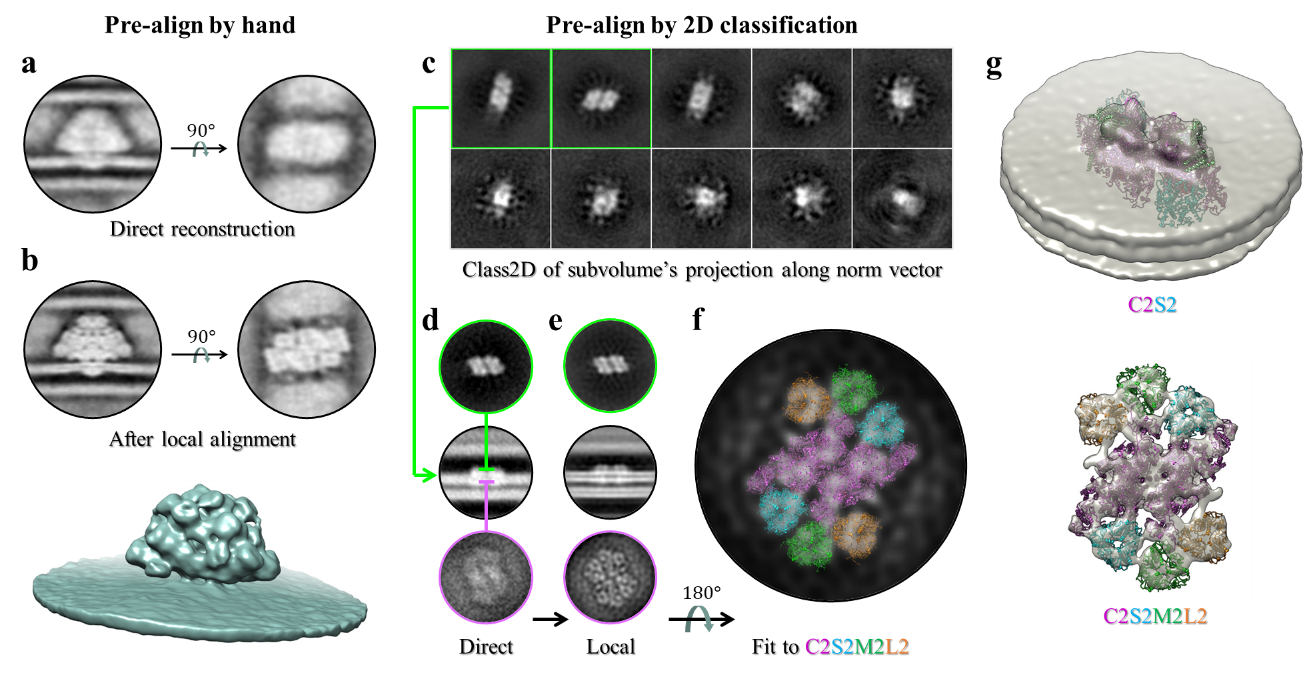
图3:通过膜蛋白的法向量和面内角约束STA的计算
清华大学生命科学学院李雪明副教授为本文的通讯作者。清华大学生命科学学院2020级博士生颜啸峰为该论文的第一作者。清华大学电子工程系的李树东、黄炜琳,生命科学学院的王皓博士(已毕业),电子工程系的赵天放、黄铭涛,冷冻电镜平台的周昵昀博士,以及电子工程系的沈渊教授也为本研究做出了重要贡献。本研究工作获得了国家自然科学基金委、生命科学联合中心、北京生物结构前沿研究中心等的资金支持,并得到了国家蛋白质科学研究(北京)设施清华基地的技术支持。
论文链接:https://doi.org/10.1038/s41467-024-55767-w
软件链接:https://thuem.net/software/mpicker/overview.html